IsoNet:基于稳定同位素示踪代谢组学技术开发的新策略
2026-04-03 来源:MCE 中国 点击次数:21Section.01
Nature 子刊: IsoNet 策略
目前仍有超过 30% 的人类基因功能未被明确注释,其中相当一部分被推测编码代谢相关酶类。虽然基于体外酶活性的代谢组学筛选技术可用于发现未知反应,但其回收率普遍较低 (通常低于 20%) ,难以实现系统性覆盖,且多数反应无法在生理环境下得到验证。这些“缺失”的反应构成了代谢网络中的“暗物质”,严重制约了我们对细胞生理及疾病机制的系统性认知[1]。
值得关注的是,研究开发的 IsoNet (Isotopologue Similarity Networking) 策略,通过整合稳定同位素示踪代谢组学与同位素异构体模式相似性网络分析,可在无先验假设的前提下,直接从活细胞及动物体内推断并验证未知代谢反应。该方法无需酶纯化,有效规避了体外筛选的低回收率瓶颈,显著拓展了可检测反应的类型与范围——包括非酶促反应。通过系统构建同位素相似性网络,IsoNet 实现了代谢反应的高通量发现与功能解析,为绘制完整代谢图谱、揭示代谢通路在生理与病理过程中的作用提供了强大的无偏倚工具。
在代谢反应网络中,反应步骤超过 7 步的代谢物对被定义为非反应对。原始数据以源数据文件的形式提供(图 1)。
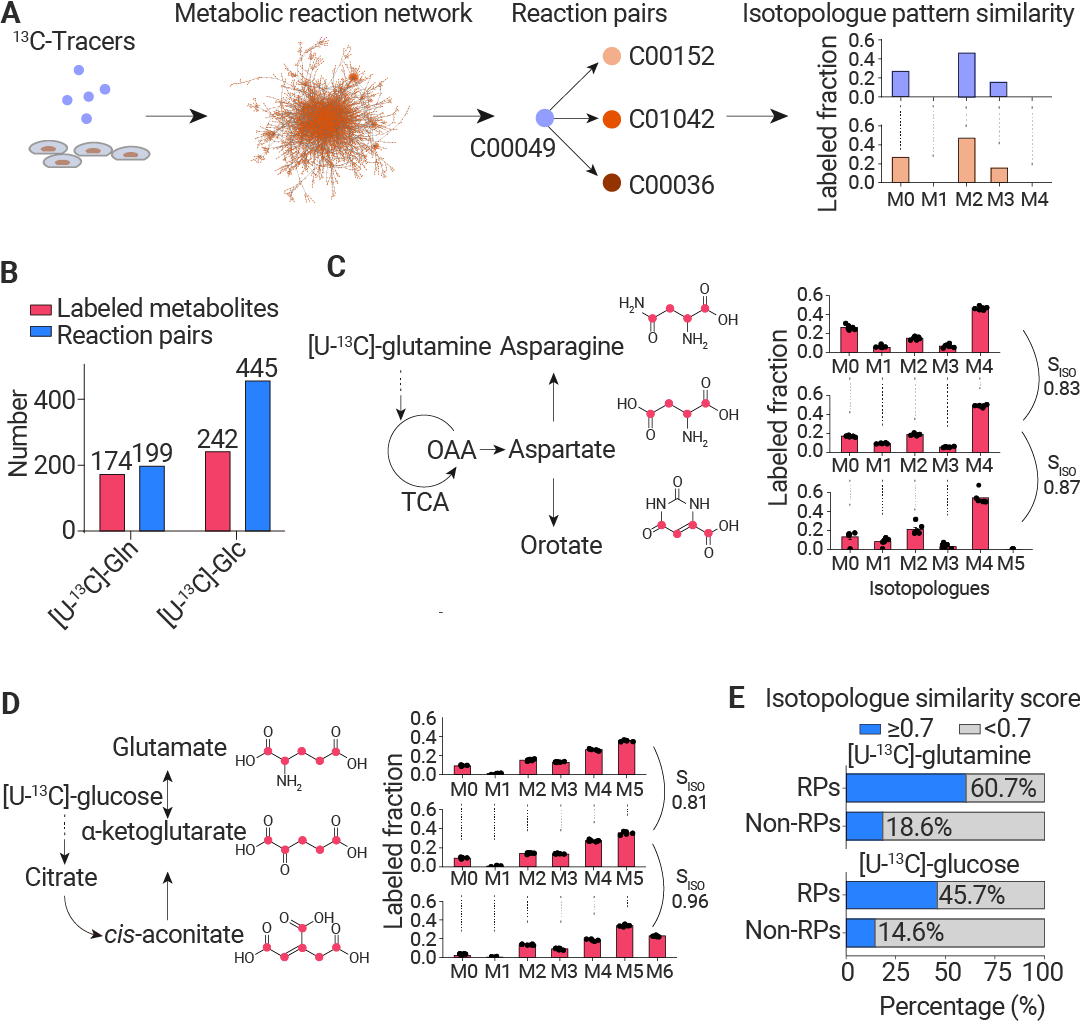
图 1.在稳定同位素示踪代谢组学中,反应相关的代谢物往往具有相似的同位素异构体模式。
A. 代谢反应相关代谢物生成示意图及其同位素异构体模式相似性计算。B. 在用全碳13 标记谷氨酰胺或 全碳13 标记葡萄糖标记 17 小时的 293T 细胞中检测到的标记代谢物和反应对的数量。C. 在用全碳13标记谷氨酰胺标记的 293T 细胞中,反应相关代谢物 (天冬酰胺/天冬氨酸和天冬氨酸/乳清酸) 的同位素异构体模式相似性评分 (SISO) (每组 n = 6 个生物学重复)。数值表示平均值 ± 标准误。D. 在用全碳13标记葡萄糖标记的 293T 细胞中,反应相关代谢物 (谷氨酸/α-酮戊二酸和 α-酮戊二酸/顺式乌头酸)的同位素异构体模式相似性评分 (SISO) (每组 n = 6 个生物学重复)。数值表示平均值 ± 标准误。E. 在用全碳13标记谷氨酰胺或全碳13标记葡萄糖标记的 293T 细胞中,反应对 (RP) 和非反应对 (non-RP) 中两种代谢物具有高同位素异构体相似性评分 (SISO ≥ 0.7) 的百分比。
Section.02
核心成果:
从"已知地图"走向"未知大陆"
该研究的主要成果可以概括为三点:
『1. 提出 IsoNet 方法学框架』
研究发现,在稳定同位素示踪实验中,具有直接生化转化关系的底物与产物,其同位素异构体分布模式 (isotopologue patterns) 高度相似。基于此,团队开发了同位素模式相似性评分 (SISO score),并以此构建代谢物间的关联网络,从而在全代谢组层面无偏倚地推断潜在代谢反应。
『2. 系统发现数百个潜在新代谢反应』
在 HEK293T 细胞、小鼠肝脏及诱导性骨髓来源巨噬细胞 (iBMDM) 中,IsoNet 共推断出数百对具有高置信度的代谢物转化关系,涵盖氧化还原、基团转移、水解、连接等多种反应类型。其中大量反应未被收录于 KEGG、HMDB 或 MetaCyc 等主流代谢数据库。
『3. 重构谷胱甘肽代谢子网络』
研究聚焦于谷胱甘肽 (GSH) 相关代谢网络,发现 GSH 可通过一种新型转硫反应 (transsulfuration),将其半胱氨酸残基替换为丝氨酸,直接生成新代谢物 γ-谷氨酰-丝氨酰-甘氨酸 (γ-Glu-Ser-Gly)。该结果表明,谷胱甘肽不仅是经典抗氧化剂,还可作为内源性硫供体参与代谢调控。这一发现挑战了传统认为 γ-谷氨酰三肽仅通过 ATP 依赖的连接酶合成的认知。
Section.03
稳定同位素标记物:
研究的"发动机"
IsoNet 能够成立的前提,是高质量的稳定同位素示踪数据。该研究系统使用了多种碳 13 标记化合物,它们均为全碳 13 标记的化合物如:全碳 13 标记葡萄糖 (D-Glucose-13C6)、全碳 13 标记谷氨酰胺 (L-Glutamine-13C5)、全碳 13 标记乙酸 (Acetic acid-13C2) 、全碳 13 标记丝氨酸 (L-Serine-13C3)、全碳 13 标记半胱氨酸 (L-Cysteine-13C3)、全碳 13 标记甘氨酸 (Glycine-13C2)、全碳 13 标记的丙酮酸钠 (Pyruvic acid-13C3 sodium) 等。
这些全碳 13 标记化合物,覆盖了糖酵解、TCA 循环、氨基酸代谢和谷胱甘肽合成等关键代谢通路,使研究者能够根据碳 13 标记原子追踪其在复杂网络中的去向。
与传统同位素实验只验证单条假设通路不同,本研究关注的是所有代谢物的同位素分布形态。只要两个代谢物在细胞中存在直接反应关系,它们的同位素“指纹”就会呈现高度相似性,这正是 IsoNet 的逻辑基础。这也是 IsoNet 对实验结果做分析的重要依据。
Section.04
同位素标记:实验流程
从研究者设计的实验操作来看,该研究为稳定同位素示踪提供了一个可复制、可扩展的范式,也为后续的研究提供了较好的指导范例,以下为以细胞为例作者做实验的详细流程:
1. 细胞培养与标记条件
细胞系:293T 细胞、iBMDM (永生化骨髓源性巨噬细胞) 等。培养基:使用含 10% 透析胎牛血清 (dFBS) 和 1% 青霉素-链霉素的 DMEM。标记时机:细胞生长至 80% 汇合度时更换为含同位素标记物的新鲜培养基。标记时间:通常为 17 小时 (可根据实验调整)。
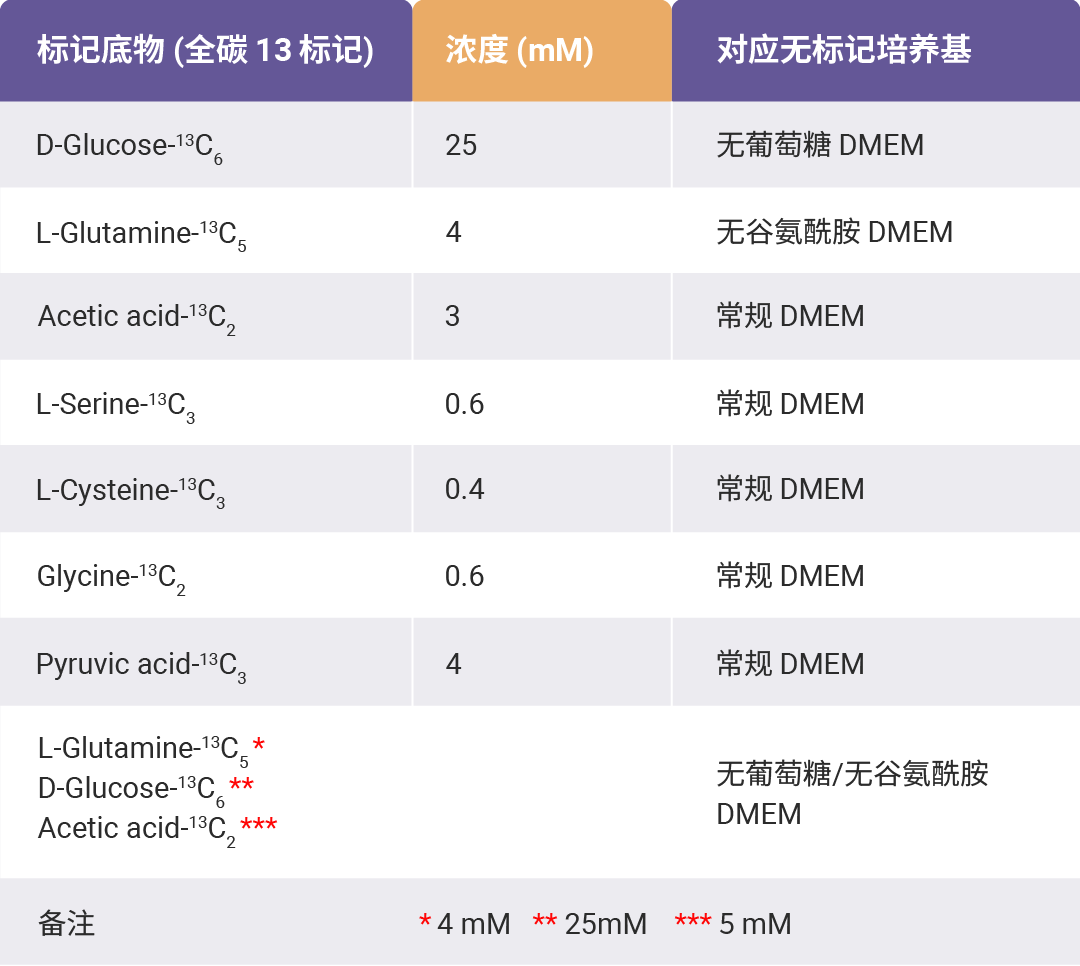
2. 标记物浓度
表格 1. 单一/混合标记底物使用浓度计培养基
3. 代谢淬灭与提取
快速移除培养基,用 PBS 洗涤细胞两次。置于干冰上,加入预冷的代谢提取液 (甲醇/水 = 80/20,V/V) 淬灭代谢。 ?80 ℃ 孵育 40 分钟。刮取细胞并转移至离心管,再用 400 μL 提取液清洗培养皿,合并提取液。涡旋 1 分钟,4 ℃、16200 × g 离心 10 分钟,取上清。如测定半胱氨酸等易氧化代谢物,可取部分上清进行 N-乙基马来酰亚胺 (NEM) 衍生化处理。剩余上清在真空浓缩仪中 4 ℃ 干燥,?80 ℃ 保存。
4. 样本前处理
干燥样本用 100 μL 乙腈:水 (1:1,v/v) 复溶。超声 10 分钟,4 ℃、16200 × g 离心 15 分钟。取上清进行 LC-MS 分析。
5. 数据预处理
原始数据经 ProteoWizard 转换为 mzXML (MS1) 和 mgf (MS2) 格式。 使用 xcms 进行峰检测与对齐。通过 MetDNA 进行已知代谢物注释 (MSI Level 1-2)。未知特征峰经 CAMERA 去冗余、Genform 预测分子式。使用 MetTracer 提取标记代谢物的同位素分布。采用 Accucor 进行天然同位素校正。
6. IsoNet 分析
A. 同位素相似性网络构建:计算代谢物对的同位素模式相似性得分 (Siso)。结合 MS/MS 谱图相似性 (余弦得分)。构建网络:节点为标记代谢物,边表示 Siso > 0.7 且 MS2 相似性 > 0.5。
B. 反应推断与注释:利用 KEGG 反应库和 Delta Mass 库匹配代谢物对的质量差 (Δm/z)。推断反应类型 (如氧化、转移、水解等) 及原子差异。
7. 验证实验
A. 化学标准品验证:合成新发现代谢物 (如 γ-Glu-Ser-Gly、S-乙酰谷胱甘肽等)。通过保留时间、MS/MS 谱图及核磁共振 (NMR) 比对确认结构。
B. 能与机制验证:抑制剂处理:使用 BSO (谷胱甘肽合成抑制剂) 验证代谢物与谷胱甘肽代谢通路的关联。基因敲降:通过 siRNA 敲低 GCS (谷氨酰半胱氨酸合成酶),观察代谢物水平变化。体外反应验证:在无酶体系中孵育底物 (如谷胱甘肽 + 乙酰辅酶 A),验证非酶促反应。分类为已知反应、I 型未知反应 (已知-未知代谢物对)、II 型未知反应 (未知-未知代谢物对)。
该实验流程的优势在于:无需提前设定靶点,真正实现数据驱动的反应发现。
Section.05
小结
IsoNet 解决的问题:突破“已知代谢物-已知反应”的研究边界;将稳定同位素示踪从假设验证工具升级为无偏倚发现引擎;系统揭示非经典、非酶促或低丰度代谢反应。如需更多同位素标记物请参考 MCE 官网。

|
葡萄糖全 13C 标记物,可示踪与葡萄糖相关的合成分解代谢研究 |
|
谷氨酰胺全 13C 标记物,可示踪与谷氨酰胺相关的合成分解代谢研究 |
|
乙酸全 13C 标记物,代谢产物及途径的分析 |
|
乙酸钠全 13C 标记物,代谢产物及途径的分析 |
|
乙酸钠全 13C 标记物,代谢产物及途径的分析 |
|
L-半胱氨酸全 13C 标记物,代谢产物及途径的分析 |
|
甘氨酸全 13C 标记物,代谢产物及途径的分析 |
|
丙酮酸全 13C 标记物,代谢产物及途径的分析 |

[1] Gao Y, etal. Charting unknown metabolic reactions by mass spectrometry-resolved stable-isotope tracing metabolomics. Nat Commun. 2025 May 31;16 (1):5059



